商机详情 -
多组学整合空间多组学售后服务
革新免疫研究,绘制免疫应答全景图谱** 免疫系统的精细应答依赖免疫细胞的空间募集与分子协同作用,传统研究难以捕捉这一动态空间过程。Bruker空间多组学技术可同步检测免疫身体内部、影响或liu组织中免疫细胞的亚型分布、细胞因子表达及信号通路状态。在细菌影响研究中,能清晰呈现肺部组织中巨噬细胞、T细胞的浸润区域及抗病毒因子的空间表达特征;在自身免疫病研究中,可定位关节滑膜组织中炎症因子的高表达区域与免疫细胞的异常聚集模式。检测过程无需体外培养细胞,保留体内真实免疫微环境,为解析免疫应答机制、开发新型疫苗与免疫改善药物提供全景式空间数据支撑。双提升通量 + 保留组织完整性,布鲁克 EpicIF 技术革新空间 proteomics。多组学整合空间多组学售后服务

助力内分泌研究,解析调控空间网络** 内分泌系统的调控具有严格的组织特异性与空间信号传递特征,异常分泌常导致局部组织分子紊乱。Bruker空间多组学技术可精细捕获内分泌身体内部(如甲状腺、肾上腺、胰腺)及靶身体内部的分子空间分布特征。在甲状腺功能亢进研究中,能清晰定位甲状腺滤泡上皮细胞中合成相关基因的表达异常;在糖尿病研究中,可解析胰岛β细胞功能异常区域的分子变化与胰岛素靶身体内部的响应模式。支持内分泌身体内部活检样本、动物模型样本检测,兼容临床样本处理流程,为内分泌疾病病因研究、精细改善提供关键数据。多组学整合空间多组学售后服务一站式空间多组学方案,布鲁克让科研数据更具说服力。
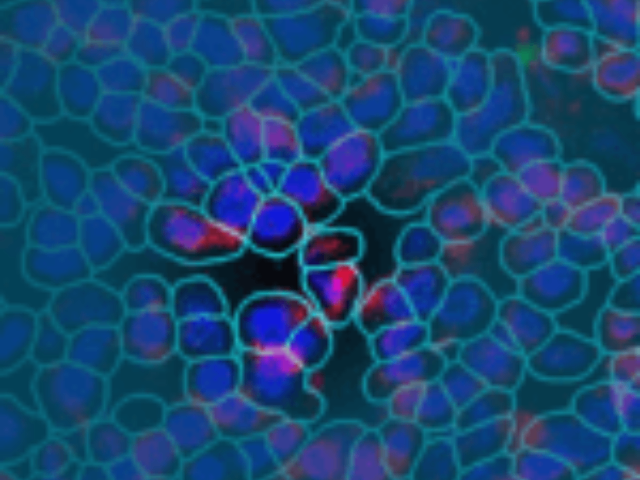
助力骨骼肌研究,解析运动与代谢调控机制** 骨骼肌的收缩功能、能量代谢及损伤修复具有明显的肌纤维类型特异性与空间调控特征。Bruker空间多组学技术可区分不同类型肌纤维(快肌、慢肌)的分子表达差异,追踪运动或损伤后的空间分子变化。在运动生理学研究中,能定位运动后肌纤维中能量代谢相关基因与蛋白的表达热点;在肌萎缩研究中,可解析肌纤维退化区域的分子调控网络与再生相关分子的分布。支持骨骼肌活检样本、动物模型样本检测,高分辨率可清晰呈现肌纤维的空间排布与分子特征,为运动医学、肌病研究及康复改善提供数据支撑。
优化药物研发,提升研发效率与成功率** 药物研发过程中,药物在组织中的分布、靶点结合效率及对不同区域的分子调控效果,是决定研发成败的关键。Bruker空间多组学技术可在药物筛选、药效评估、毒性检测等全流程提供空间维度数据。在抗liu药物研发中,能直观呈现药物在liu组织与正常组织中的分布差异,及对肿瘤细胞分子表达的空间调控效果;在大脑内部药物研发中,可精细检测药物在大脑不同脑区的渗透情况及对神经元分子功能的影响。替代传统繁琐的动物实验与体外检测组合,实现“一次检测,多维数据”,大幅缩短研发周期,降低研发成本,提升药物研发成功率。加速科研转化,布鲁克让空间生物学发现更快落地应用。

赋能病毒学研究,解析病毒影响空间机制** 病毒影响的过程涉及病毒的空间入侵、复制及宿主免疫应答的空间互作,传统病毒学研究难以捕捉这一动态空间过程。Bruker空间多组学技术可同步检测病毒在宿主组织中的空间分布与宿主分子变化。在流感病毒影响研究中,能清晰定位病毒在肺部组织的扩散路径与宿主抗病毒基因的空间表达热点;在乙肝病毒影响研究中,可解析病毒在肝脏组织中的定植区域与肝细胞损伤的分子关联。支持影响组织样本、细胞模型样本检测,高灵敏度可捕获低丰度的病毒核酸与蛋白信号,为病毒疫苗研发、抗病毒药物设计提供关键机制数据。空间原位洞察,布鲁克解锁生命科学新可能。多组学整合空间多组学售后服务
布鲁克空间多组学,让生物机制看得见、摸得透。多组学整合空间多组学售后服务
革新昆虫学研究,解析昆虫发育与抗逆机制** 昆虫的发育变异、抗药性及与植物的互作具有复杂的空间分子调控特征,传统昆虫学研究难以多面解析。Bruker空间多组学技术可对昆虫不同发育阶段(卵、幼虫、蛹、成虫)及不同组织的分子空间分布进行检测。在家蚕变异发育研究中,能清晰呈现幼虫到蛹转化过程中关键基因的空间表达变化;在蚜虫抗药性研究中,可解析杀虫剂作用靶点的空间表达异常与代谢解决毒相关分子的分布。支持昆虫整体样本、组织样本检测,样本需求量少,为昆虫资源利用、害虫防治及抗药性研究提供技术支撑。多组学整合空间多组学售后服务
冠乾科技(上海)有限公司汇集了大量的优秀人才,集企业奇思,创经济奇迹,一群有梦想有朝气的团队不断在前进的道路上开创新天地,绘画新蓝图,在上海市等地区的仪器仪表中始终保持良好的信誉,信奉着“争取每一个客户不容易,失去每一个用户很简单”的理念,市场是企业的方向,质量是企业的生命,在公司有效方针的领导下,全体上下,团结一致,共同进退,**协力把各方面工作做得更好,努力开创工作的新局面,公司的新高度,未来冠乾科技供应和您一起奔向更美好的未来,即使现在有一点小小的成绩,也不足以骄傲,过去的种种都已成为昨日我们只有总结经验,才能继续上路,让我们一起点燃新的希望,放飞新的梦想!